A relevância do treinamento
Uma etapa importante no desenvolvimento da classificação da ordem das pulgas está associada ao desenvolvimento da pesquisa genomolecular. Atualmente, graças a esses métodos, o parentesco das ordens de pulgas e mecópteros está confirmado. Os genes do DNA ribossomal, o fator de alongamento da síntese de proteínas e o gene mitocondrial citocromo oxidase II (COII), que foram estudados em representantes da maioria das famílias da ordem mecóptero, bem como 128 espécies de 83 gêneros de pulgas de 16 famílias, estão sendo estudados ativamente (S.G. Medvedev. 2009; Whiting 2002; Whiting et al. 2008). A filogenia da pulga é reconstruída com base em dados sobre esses genes por vários métodos de construção de árvores filogenéticas e modelos para calcular distâncias entre pares, que muitas vezes é apresentada na forma de uma árvore de consenso (consenso strick) (Whiting et al. 2008). No entanto, em alguns casos, os resultados dos estudos genomoleculares contradizem o esquema de laços familiares,obtidos com base na análise filogenética. Além disso, de acordo com diferentes interpretações dos dados genéticos moleculares, a origem das infraordens chave das pulgas pode ser interpretada de diferentes maneiras. Portanto, do ponto de vista de diferentes autores, os mesmos clados de pulgas podem ser grupos polifiléticos e monofiléticos (Whiting et al. 2008, S.G. Medvedev. 2019). Isso pode ser devido às peculiaridades da ecologia da fauna de pulgas moderna e a vários problemas metodológicos de se trabalhar com dados genéticos moleculares.e grupos monofiléticos (Whiting et al. 2008, S.G. Medvedev. 2019). Isso pode ser devido às peculiaridades da ecologia da fauna de pulgas moderna e a vários problemas metodológicos de se trabalhar com dados genéticos moleculares.e grupos monofiléticos (Whiting et al. 2008, S.G. Medvedev. 2019). Isso pode estar relacionado tanto às peculiaridades da ecologia da fauna moderna de pulgas quanto a vários problemas metodológicos de se trabalhar com dados genéticos moleculares.
Em relação ao primeiro ponto, deve-se enfatizar que o isolamento das linhas filéticas individuais das pulgas, que possuem igual status na taxonomia, ocorreu em diferentes intervalos históricos. Isso, por sua vez, significa que a fauna de pulgas são fragmentos espalhados de uma extensa paleofauna, que agora está em grande parte extinta (S.G. Medvedev. 2009, S.G. Medvedev. 2019). Conclui-se que, com diferentes abordagens metodológicas aos estudos genéticos moleculares, podemos perder de vista a evolução convergente das sequências de nucleotídeos (homoplasia), o que pode levar a erros na determinação da topologia da árvore e ao baixo suporte estatístico dos ramos. Então, por exemplo, usando dados que têm uma relação diferente para táxons diferentes e, consequentemente, uma relação diferente para partes diferentes dos genes,encontraremos lacunas nas sequências e a ausência de dados para diferentes loci para diferentes amostras (S.G. Medvedev. 2019, Lukashov V.V. 2006). Portanto, na escolha de um método de pesquisa, todos esses problemas devem ser levados em consideração e as amostras dos táxons de pulgas mais estudadas e comuns devem ser selecionadas para depois compará-las com as amostras de mecópteros mais estudadas. Desta forma, podemos construir uma árvore mais confiável e com alto suporte.
, Siphonaptera Mecoptera -II (COII).
:
Siphonaptera NCBI [5], .
(COX 1) Siphonaptera .
-II (COII) Mecoptera Siphonaptera NCBI [1].
MEGA X.
.
NCBI [5] : Chaetopsylla globiceps (Taschenberg, 1880), Chaetopsylla trichosa (Kohaut, 1903), Ctenocephalides felis (Bouché, 1835), Ctenocephalides canis (Curtis, 1826), Ceratophyllus sciurorum (Schrank, 1803), Leptopsylla segnis (Schönherr, 1811). , NCBI[1], Boreus: Boreus westwoodi (Hagen, 1866), Boreus hymalis (Linnaeus, 1767), Boreus coloradensis (Byers, 1955), Boreus nivoriundus (Fitch, 1847), Boreus brumalis (Fitch, 1847), Boreus californicus (Packard, 1870), (.1.).
UPGMA [2] , - 500 [3]. Muscle (. 2.) MEGA X [4]. Muscle . , . translate DNA to protein and vice versa (.3), . (. 3.) , - , . (.4). MEGA . Modeltest 3.06 PPC (Posada, D., Crandall, K.C., 1999) (AIC), . AIC , , (Posada, D., Buckley, T.R., 2004.). MEGA X [4] 64- Windows 10 Home 4- INTEL 1,6 1 .
- [6] (.5.). 12 . 1-+2-+3-+. ( ). 742 .
( 1.)

(.2.)
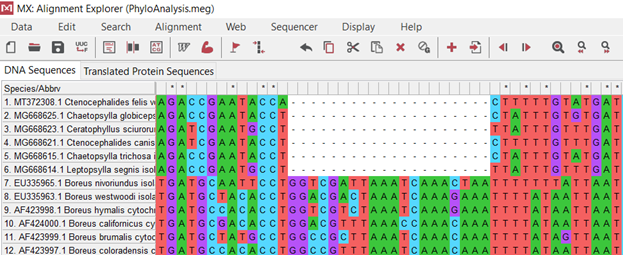
(.3.)
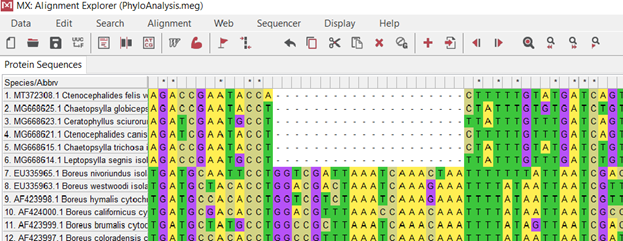
(.4.)
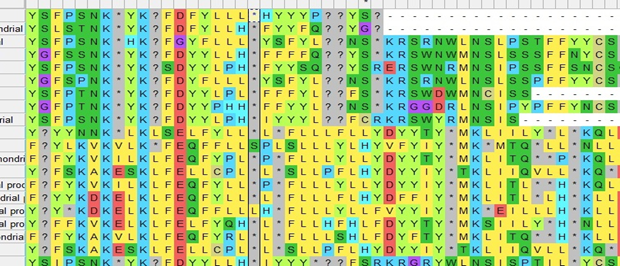
(.5)
. Mecoptera Siphonaptera. 60% , Mecoptera Siphonaptera. , , , .
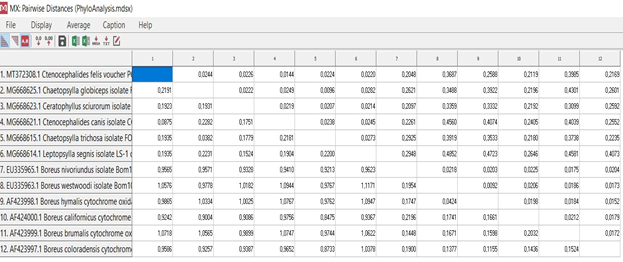
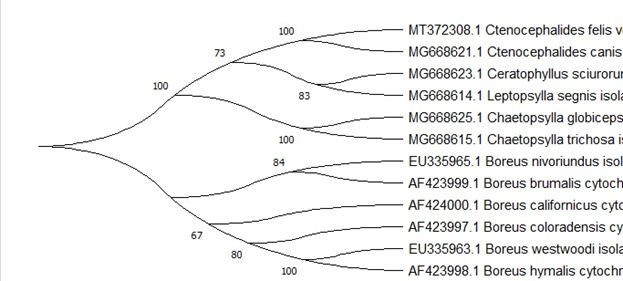
, MEGA X [4] (80%-100%) , . Ceratophyllus sciurorum Leptopsylla segnis (73%), . , (.. .2009; Whiting 2002; Whiting et al. 2008).
Mecoptera Siphonaptera . . Boreus nivoriundus Boreus brumalis (80%) «» Chaetopsylla globiceps Chaetopsylla trichosa (100%). , Mecoptera Siphonaptera. Boreus californicus (67%) . , . (.6.)
(.6.)
. . , , , . . . . [https://vk.com/phanerozoi] . , .
.
, , .
, .
1. Whiting M.F. 2002. Mecoptera is paraphyletic: multiple genes and phylogeny of Mecoptera and Siphonaptera. Zoologica Scripta, 31: 93–104
2. Whiting M.F., Whiting A.S., Hastriter M.W. and Dittmar K. 2008. A molecular phylogeny of fleas (Insecta: Siphonaptera) and host associations. Cladistics, 24: 1–31.
3. , .. , 313, № 3, 2009, c. 273–282
4. (SIPHONAPTERA) .., .. III , 2009, . 185-190
5. / .. —.. , 2009. — .256. .29-31.
6. Posada, D., Buckley, T.R., 2004. Model selection and model averaging in phylogenetics: advantages of the AIC and Bayesian approaches over likelihood ratio tests. Syst. Biol. 53, 793–808.
7. Posada, D., Crandall, K.C., 1999. Modeltest. Bioinformatics 14, 817–818.
1. http://lifemap.univ-lyon1.fr
2. Sneath P.H.A. and Sokal R.R. (1973). Numerical Taxonomy. Freeman, San Francisco.
3. Felsenstein J. (1985). Confidence limits on phylogenies: An approach using the bootstrap. Evolution 39:783-791
4. Kumar S., Stecher G., Li M., Knyaz C. e Tamura K. ( 2018 ). MEGA X: Análise Genética Evolutiva Molecular em plataformas de computação. Molecular Biology and Evolution 35 : 1547-1549.
5.https: //www.ncbi.nlm.nih.gov/pmc/articles/PMC4681159/
6. Tajima F. e Nei M. ( 1984 ). Estimativa da distância evolutiva entre sequências de nucleotídeos. Molecular Biology and Evolution 1 : 269-285.